関連記事
理研、iPS細胞ではncRNAが十分に発現していないことを明らかに
理化学研究所のピエロ・カルニンチチームリーダーらによる研究グループは、ES細胞とiPS細胞で発現する全てのRNAを比較解析し、ES細胞で発現しているノンコーディングRNAの多くが、iPS細胞では十分に発現していないことを発見した。
万能細胞と呼ばれるものの中でも、iPS細胞とES細胞は異なる状態にある可能性が報告されており、その違いを正確に理解することが、iPS細胞作製技術の改良や、臨床応用に適したiPS細胞の評価選別法の確立に繋がると考えられている。
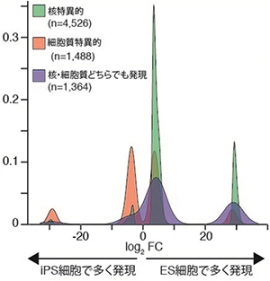
今回の研究では、マウスES細胞とマウスリンパ球から樹立したiPS細胞を用いて、全RNAを解析したところ、核内のRNAで4,526種、細胞質のRNAで1,488種、核と細胞質に共通するRNAでは1,364種、ES細胞とiPS細胞で発現に差があることが分かった。
iPS細胞では適切に誘導されていないES細胞核特異的なRNAは、その多くが、既知の塩基配列や機能との関連が不明な未知のRNAで、これらのRNAの機能を予測したところ、エンハンサーやスーパーエンハンサーなど遺伝子発現制御に関わるncRNAが多く含まれることが示唆された。
さらに、これらのエンハンサーやスーパーエンハンサーが発現を制御している可能性のある約200遺伝子の発現を、ES細胞とiPS細胞で比較したところ、ES細胞での発現量がiPS細胞の2倍以上となっている遺伝子が多く、エンハンサー量の違いが遺伝子発現に大きな影響を及ぼしていることが確認できた。
今後は、本研究成果がiPS細胞を適切に評価する方法の開発やiPS細胞作製技術の改良に貢献すると期待されている。
なお、この内容は「ell Cycle」に掲載された。
スポンサードリンク